“要理解蛋白质复合物的功能的分子机制,生物学家一直使用诸如X射线和显微镜等实验方法,但它们是时间和资源密集的努力,”生物科学教授和计算机科学教授Daisuke Kihara说Purdue’s College of Science, who leads the research team. “Bioinformatics researchers in our lab and other institutions have been developing computational methods for modeling protein complexes. One big challenge is that a computational method usually generates thousands of models, and choosing the correct one or ranking the models can be difficult.”
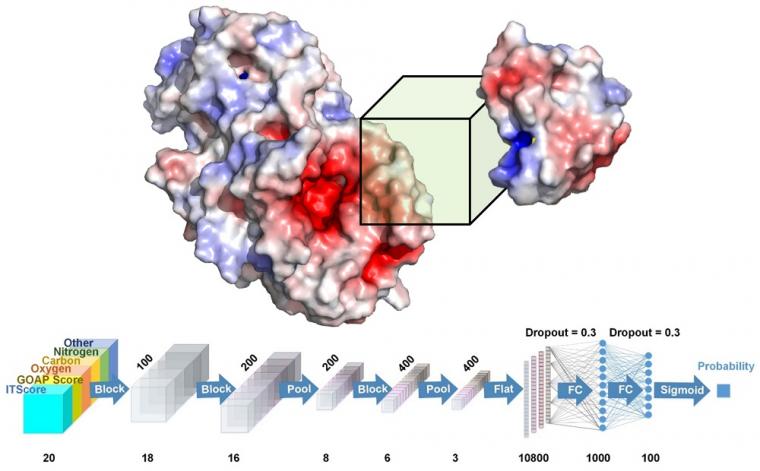
木原和他的团队开发了一个名为DOVE的系统,利用基于体素的深度神经网络对诱饵进行对接选择,该系统将深度学习原理应用于蛋白质相互作用的虚拟模型。DOVE通过扫描模型的蛋白质-蛋白质界面,利用深度学习模型原理,区分和捕捉正确和不正确模型的结构特征。
“我们的工作代表了生物信息学领域的重大进步,”研究生和研究团队成员的小王说。“这可能是第一次研究人员已成功使用深度学习和3D功能,以快速了解某些蛋白质模型的有效性。然后,该信息可用于创建靶向药物以阻止某些蛋白质蛋白质相互作用。“
来源:普渡大学