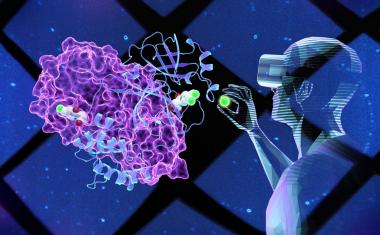
一个SARS-CoV-2被称为主要蛋白酶(Mpro)的酶是一个有希望的目标,在寻找新的抗病毒治疗方法。阻止主要蛋白酶工作的分子——称为酶抑制剂——阻止病毒繁殖,所以可能是有效的药物。世界各地的研究人员正在努力寻找这种分子。药物有效性的一个关键预测指标是它与靶标的结合紧密程度;了解药物如何与蛋白质相适应,有助于研究人员设计改变其结构,使其结合得更紧密。
来自布里斯托尔大学化学学院的Adrian Mulholland教授是这项研究的第一作者,他解释说:“我们已经证明了交互式虚拟现实可以模拟病毒蛋白质和抑制剂是如何与酶结合的。研究人员可以使用这个工具来帮助理解酶是如何工作的,也可以看到潜在的药物是如何融入酶的。这将有助于设计和测试新的潜在药物先导物。我们正在与整个社区分享这些模型。”
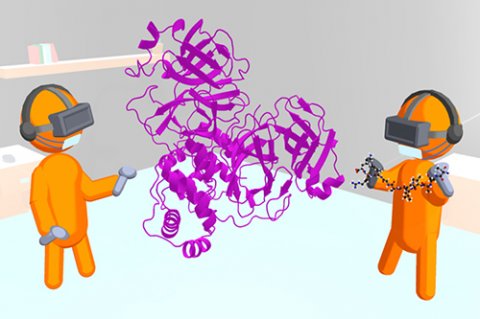
布里斯托尔的研究小组已经开发了一个用于交互式“分子动力学”模拟的虚拟框架。它是开源的软件Narupa使用现成的VR设备。
在这项研究中,布里斯托尔团队创造了一个三维模型并在虚拟现实(iMD-VR)中使用交互式分子动力学模拟“进入”它,并以原子细节显示与酶结合的分子。结果表明,使用者能够展示药物分子如何与酶相适应。
穆赫兰教授补充说:“目前全球有许多努力旨在确定药物的先导新型冠状病毒肺炎.我们的iMD-VR工具将是一种宝贵的资源,为国际药物发现社区提供虚拟合作,帮助预测潜在药物如何与SARS-CoV-2靶标结合。一个令人兴奋的方面是,它还允许研究人员以新的方式合作:使用云计算他们可以在不同的地点——甚至可能是不同的国家——同时在相同的虚拟分子环境中工作,同时解决药物发现问题。”
“药物如何与SARS-CoV-2刺突蛋白结合的计算模型在推进全球抗击疫情方面至关重要。Narupa将虚拟现实中的分子动力学模拟带到一个全新的水平。”“我们很高兴甲骨文的高性能云基础设施支持了这一创新框架的开发,现在正在帮助推动全球互联努力抗击COVID-19。发展一个由云研究人员组成的互联社区正是Oracle for Research的初衷。”
这项研究发表在化学信息与建模杂志.
来源:布里斯托大学